组蛋白赖氨酸甲基化修饰作为最重要的表观遗传修饰之一,在不同物种中的功能是相对保守的。不同位点上的赖氨酸甲基化(组蛋白H3第4,9,27,36,79以及H4第20位赖氨酸残基)或是同一位点不同程度的甲基化(me1, me2, me3)代表着不同的染色质状态,进而影响基因的转录。尽管组蛋白赖氨酸甲基化修饰的功能在不同物种中相对保守,但某些修饰在动、植物基因组上的分布模式却存在差异,暗示了植物中存在特殊的组蛋白甲基化修饰的建立机制。
董爱武课题组7月5日在线发表于《Nature Communications》的研究论文,解析了单子叶模式植物水稻中组蛋白H3第36位赖氨酸三甲基化(H3K36me3)修饰建立的分子机制。研究首先分析了不同物种中H3K36me3的分布情况,包括单细胞酵母、无脊椎动物线虫和果蝇、脊椎动物小鼠和人类、高等植物拟南芥和水稻,结果显示不同于其他物种,高等植物中H3K36me3主要分布在基因体(gene body)的5’端。为了探索植物H3K36me3特异分布模式的建立机制,利用酵母双杂交系统,以水稻中主效的H3K36me3甲基转移酶SDG725作为诱饵蛋白,筛选出与之结合的转录因子OsSUF4,生化实验进一步证明了SDG725与 OsSUF4的体外、体内相互作用。遗传分析发现OsSUF4缺失的水稻植株表现出与SDG725下调植株一致的晚花表型;与晚花表型相一致,开花关键调节因子成花素基因RFT1与Hd3a在突变体中的表达降低。染色质免疫沉淀(ChIP)实验证明了OsSUF4与SDG725蛋白以相互促进的方式结合在RFT1与Hd3基因的染色质区域并通过建立H3K36me3促进基因转录。此外,利用EMSA技术,鉴定了转录因子OsSUF4特异结合的DNA元件(5’-CGGAAAT-3’);分析水稻基因组序列发现水稻中有3000多个基因在启动子区域包含这一顺式元件。ChIP-seq结合RNA-seq分析发现,OsSUF4的下调在全基因组范围内影响了一批包含该DNA元件的基因的H3K36me3修饰水平和转录水平,进一步表明OsSUF4可以通过招募SDG725促进 H3K36me3修饰的建立。最后,通过分析OsSUF4锌指结构域的晶体结构,发现了锌指结构域中负责结合靶DNA的关键氨基酸。因此该研究通过生物信息学、生物化学、遗传学以及结构生物学等多种研究手段揭示了植物H3K36me3甲基化修饰在基因体5’端建立的一种分子机制。
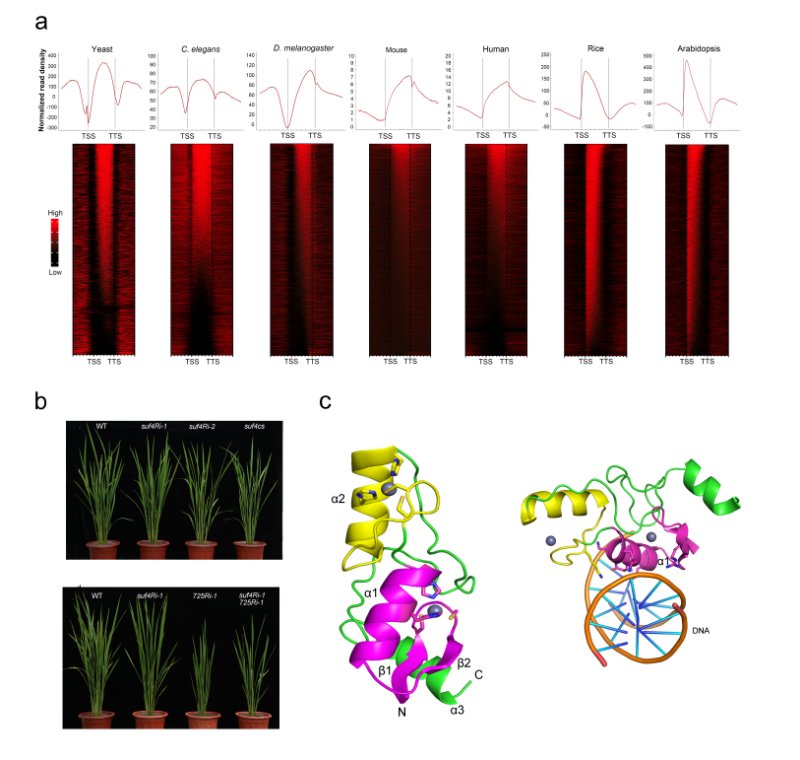
a) ChIP-seq分析显示不同物种中H3K36me3修饰的分布模式不同,
b) OsSUF4下调突变体表现出与SDG725下调突变体一致的晚花表型,c) OsSUF4的晶体结构
董爱武教授课题组的博士后刘兵为论文的第一作者,董爱武教授和俞瑜副教授为通讯作者。相关研究得到了国家自然科学基金的资助。
全文链接 https://www.nature.com/articles/s41467-019-10850-5

